Pre-Requisitos:
- Base en bioquímica o ciencias afines (bioquímica, biología, química o biotecnología).
- Haber cursado química general y química orgánica; se valora una introducción a bioquímica (idealmente con énfasis en proteínas).
- No se requiere experiencia computacional previa, pero sí interés en aprender herramientas computacionales.
Saul J. Flores
Bioquímica Computacional: Modelado, Docking y Simulaciones de Macromoléculas.
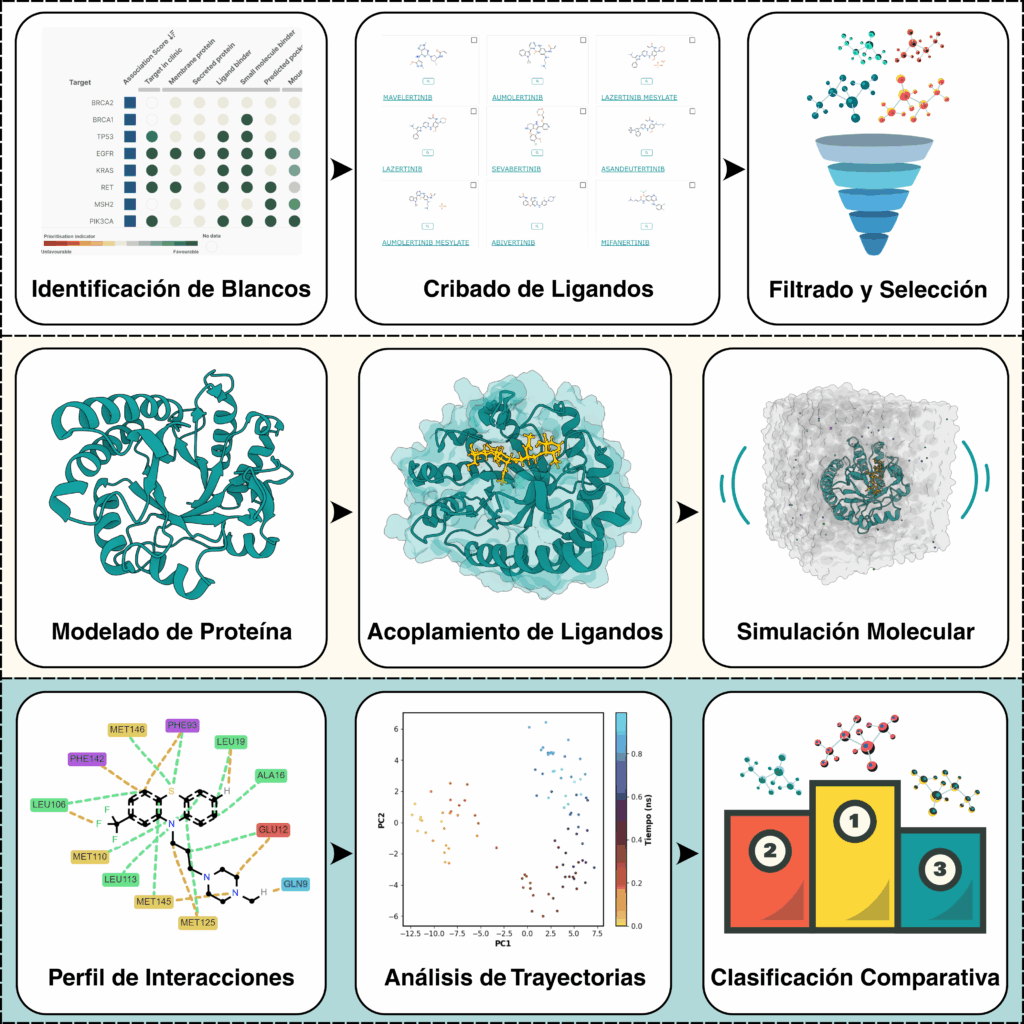
Descripción del taller: Este taller de tres días está diseñado para estudiantes de últimos años de licenciatura que desean iniciarse en la bioquímica computacional de manera práctica y accesible. Todas las actividades se realizarán directamente en el navegador utilizando plataformas gratuitas, sin necesidad de instalaciones complejas ni equipos especializados.
El taller comenzará con la exploración de bases de datos biomoleculares para aprender a visualizar y analizar estructuras de proteínas y otras macromoléculas. Posteriormente, se introducirán flujos de trabajo guiados para preparar sistemas biomoleculares, generar modelos de interacción proteína-ligando y evaluar la afinidad y plausibilidad de dichas interacciones. En la última parte, los participantes usarán un complejo proteína-ligando para ejecutar una simulación corta y aprender a interpretar métricas básicas de estabilidad estructural y dinámica.
El enfoque es completamente práctico, con cuadernos interactivos y código inicialmente oculto que los estudiantes podrán revisar y modificar si lo desean. Además, los equipos desarrollarán un mini-proyecto en el cual seleccionarán una proteína pequeña y un fármaco conocido para aplicar lo aprendido. El objetivo es que los estudiantes adquieran habilidades reproducibles que puedan extender a futuros proyectos de investigación en biotecnología y biofarmacia.
